3′ mRNAseq : Analyse Transcriptomique par Séquençage Rationalisé des extrémités 3’ des ARN
Découvrez le nouveau service proposé par GeT-TriX pour quantifier l’expression de gènes codants et suffisant pour l’analyse d’expression différentielle de gènes sans a priori. Une solution à la fois performante et économique !
AVANTAGES DU 3’mRNAseq
- Séquençage rationalisé des extrémités 3’ des ARN messagers
- 6 fois moins de données / couts de séquençage ↘
- Performant sur le sang : utilisation de bloqueurs de globine (disponible Humain, Porc)
- Echantillonnage non létal / Possibilité suivi longitudinal
- Applicable sur de faibles quantités/qualités de matériel
- Applicable sur un grand nombre d’individus : multiplexage
POUR ALLER PLUS LOIN
👉 Explorez le data paper : Transcriptomic data of piglet blood compartments with 3′ mRNA sequencing.
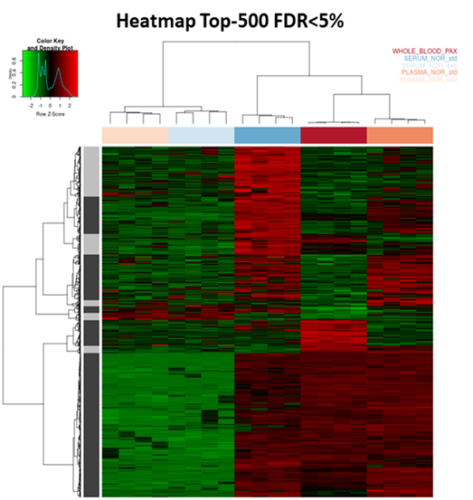
Ce travail a été réalisé en collaboration avec l’équipe REGLISS (UMR GenPhySE) et illustre le potentiel de cette stratégie pour des analyses transcriptomiques à grande échelle et comparatives. L’article présente un jeu de données transcriptomiques obtenu sur divers compartiments sanguins chez le cochon, généré par séquençage rationalisé des extrémités 3′ des ARN (3′ mRNAseq).
📌~10 000 gènes détectés dans le sang total avec bloqueur de globine
📌 Bien que le protocole ne soit pas initialement préconisé pour sérum et plasma, nous avons pu détecter respectivement ~ 6 000 et ~ 8 000 gènes
📌 ~1 000 gènes dans les exosomes extraits à partir de sérum ou plasma
Merci au Carnot France Futur Elevage pour le soutien financier accordé pour la mise en place de cette méthodologie.
N’hésitez pas nous contacter pour plus d’informations au sujet de cette technologie 3’ mRNAseq ou pour discuter de vos projets.

